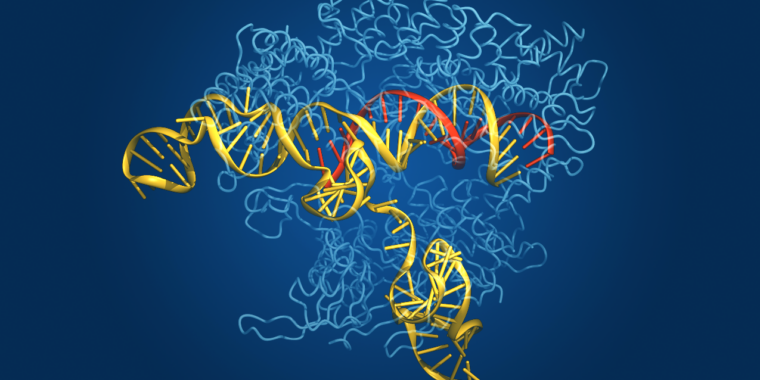
CRISPR – repetições palindrômicas curtas agrupadas e regularmente interespaçadas – é a resposta do mundo microbiano à imunidade adaptativa. As bactérias não geram anticorpos quando são invadidas por patógenos e depois bloqueiam esses anticorpos se encontrarem novamente o mesmo patógeno, como nós. Em vez disso, integram parte do ADN do agente patogénico no seu genoma e ligam-no a uma enzima que podem utilizar para reconhecer a sequência de ADN do agente patogénico e cortá-la em pedaços se o agente patogénico reaparecer.
A enzima que faz o corte chama-se Cas, em homenagem a CRISPR. Embora o sistema CRISPR-Cas tenha evoluído como um mecanismo de defesa bacteriana, foi aproveitado e adaptado pelos investigadores como uma ferramenta poderosa para manipulação genética em estudos laboratoriais. Também comprovou os seus usos agrícolas, e o primeiro tratamento baseado em CRISPR foi aprovado no Reino Unido para tratar a doença falciforme e a beta-talassemia dependente de transfusão.
Agora, os pesquisadores desenvolveram uma nova maneira de pesquisar genomas de sistemas semelhantes ao CRISPR-Cas. Eles descobriram que poderíamos ter muitas ferramentas adicionais com as quais trabalhar.
Modificação de DNA
Até o momento, seis tipos de sistemas CRISPR-Cas foram identificados em diferentes micróbios. Embora difiram nos detalhes, todos têm o mesmo apelo: entregam proteínas a uma sequência específica de material genético com um grau de especificidade que até agora tem sido tecnicamente difícil, caro e demorado de alcançar. Qualquer sequência de DNA de interesse no sistema pode ser programada e direcionada.
Os sistemas nativos dos micróbios normalmente trazem uma exonuclease – uma enzima que cliva o DNA – para a sequência, cortando o material genético dos patógenos. Esta capacidade pode ser usada para cortar qualquer sequência de DNA escolhida para edição genética; Combinado com enzimas e/ou outras sequências de DNA, pode ser usado para inserir ou excluir sequências curtas adicionais e para corrigir genes mutantes. Alguns sistemas CRISPR-Cas cortam moléculas específicas de RNA em vez de DNA. Eles podem ser usados para eliminar RNA causador de doenças, como os genomas de alguns vírus, da mesma forma que são eliminados em bactérias nativas. Isto também pode ser usado para resgatar defeitos no processamento de RNA.
Mas existem muitas maneiras adicionais de modificar ácidos nucléicos que podem ser úteis. É uma questão em aberto se as enzimas que fazem modificações adicionais evoluíram. Então alguns pesquisadores decidiram procurá-los.
Pesquisadores do MIT desenvolveram uma nova ferramenta para detectar matrizes CRISPR variantes e aplicaram-na a 8,8 tera (1.012) pares de bases de informação genômica procariótica. Muitos dos sistemas que encontraram são raros e só apareceram no conjunto de dados nos últimos 10 anos, destacando a importância de continuar a adicionar amostras ambientais anteriormente difíceis de obter a estes repositórios de dados.
A nova ferramenta era necessária porque as bases de dados de sequências de proteínas e ácidos nucleicos estão a expandir-se a um ritmo ridículo, pelo que as técnicas para analisar todos esses dados precisam de acompanhar. Alguns dos algoritmos usados para analisá-los tentam comparar cada sequência com todas as outras sequências, o que é claramente insustentável quando se lida com bilhões de genes. Outros baseiam-se no agrupamento, mas apenas encontram genes que são altamente semelhantes, pelo que não podem esclarecer as relações evolutivas entre proteínas distantemente relacionadas. Mas o agrupamento rápido e sensível à localização baseado em hashtag (“flash assembly”) funciona agrupando bilhões de proteínas em conjuntos menores e maiores de sequências que diferem apenas ligeiramente para identificar parentes novos e raros.
Uma pesquisa usando FLSHclust extraiu com sucesso 188 novos sistemas CRISPR-Cas.
Muita CRISPyness
Alguns temas surgiram do trabalho. Uma delas é que alguns dos sistemas CRISPR recentemente identificados usam enzimas Cas com domínios que nunca foram vistos antes, ou parecem ser fusões com genes conhecidos. Os cientistas também caracterizaram algumas dessas enzimas e descobriram que uma é mais específica do que as enzimas CRISPR atualmente em uso, e outra corta o RNA que eles propõem ser estruturalmente distinto o suficiente para incluir um sistema CRISPR-Cas tipo 7 inteiramente novo.
Um corolário deste tópico é ligar enzimas com funções diferentes, não apenas nucleases (enzimas que cortam DNA e RNA), com matrizes CRISPR. Os cientistas exploraram a notável capacidade do CRISPR de atingir genes, ligando-o a outros tipos de enzimas e moléculas, como corantes fluorescentes. Mas aparentemente a evolução chegou primeiro.
Por exemplo, FLSHclust identificou algo chamado transposase que está associado a dois tipos diferentes de sistemas CRISPR. A transposase é uma enzima que ajuda a transferir uma parte específica do DNA para outra parte do genoma. A transformação dirigida por RNA CRISPR já foi vista antes, mas este é outro exemplo disso. Toda uma gama de proteínas com diferentes funções, como proteínas com domínios transmembranares e moléculas sinalizadoras, foi encontrada associada a matrizes CRISPR, destacando a natureza mista da evolução desses sistemas. Eles até encontraram uma proteína expressa por um vírus que se liga às matrizes CRISPR e as torna inativas, com o vírus essencialmente desativando o sistema CRISPR que evoluiu para proteger contra vírus.
Os pesquisadores não apenas encontraram novas proteínas associadas a matrizes CRISPR, mas também encontraram outras matrizes repetidas regularmente espaçadas que não estavam associadas a nenhuma enzima Cas, semelhante ao CRISPR, mas não ao CRISPR. Eles não têm certeza da função desses sistemas guiados por RNA, mas especulam que eles estão envolvidos na defesa, assim como o CRISPR.
Os autores decidiram encontrar “uma lista de proteínas guiadas por RNA que expanda nossa compreensão da biologia e evolução desses sistemas e forneça um ponto de partida para o desenvolvimento de novas biotecnologias”. E parecem ter alcançado o seu objetivo: “Os resultados deste trabalho revelam flexibilidade regulatória e funcional e modularidade sem precedentes dos sistemas CRISPR”, escrevem. E concluem: “Isto representa apenas uma pequena fração dos sistemas descobertos, mas destaca a amplitude do potencial inexplorado da biodiversidade da Terra.” Os restantes candidatos servirão como recurso para exploração futura.
Artigo DOI: 10.1126/science.adi1910